主要职责
中国科学院贯彻落实党中央关于科技创新的方针政策和决策部署,在履行职责过程中坚持党中央对科技工作的集中统一领导。主要职责是:
一、开展使命导向的自然科学领域基础研究,承担国家重大基础研究、应用基础研究、前沿交叉共性技术研究和引领性颠覆性技术研究任务,打造原始创新策源地。 更多+
院况简介
中国科学院是国家科学技术界最高学术机构、国家科学技术思想库,自然科学基础研究与高技术综合研究的国家战略科技力量。
1949年,伴随着新中国的诞生,中国科学院成立。建院70余年来,中国科学院时刻牢记使命,与科学共进,与祖国同行,以国家富强、人民幸福为己任,人才辈出,硕果累累,为我国科技进步、经济社会发展和国家安全作出了不可替代的重要贡献。 更多+
院领导集体
科技奖励
科技期刊
科技专项
科研进展/ 更多
工作动态/ 更多
工作动态/ 更多
中国科学院学部
中国科学院院部

语音播报

基因组DNA和组蛋白以特定的形式高度折叠在细胞核中,这一高级结构即三维基因组学,对细胞核内的诸多生命活动至关重要。基于染色质构象捕获(3C),尤其是高通量技术(Hi-C,ChIA-PET)的发展推动了三维基因组的研究,发现了包括染色质拓扑相关结构域(TAD),染色质环等一系列层次化的结构特征。近年来,单细胞水平下的Hi-C研究成为三维基因组的重要研究方向。单细胞Hi-C数据对深入理解染色质结构的动力学机制,建立高分辨率细胞发育图谱都具有重要意义。然而,单细胞Hi-C数据由于极度稀疏,目前主流的Hi-C数据分析算法对其无能为力,而针对单细胞Hi-C设计的算法亦表现不佳。因此,亟须新的计算方法来分析鉴定单细胞内的染色质高级结构。
7月27日,中国科学院北京基因组研究所(国家生物信息中心)张治华研究组开发了预测单细胞内类TAD结构的算法deTOKI。相关研究成果以DeTOKI identifies and characterizes the dynamics of chromatin TAD-like domains in a single cell为题,发表在Genome Biology上。
该研究将deTOKI与适用于低分辨率水平Hi-C数据的新算法IS、deDoc、SpectralTAD、GRiNCH,以及先由单细胞Hi-C实验数据通过预测出高分辨率数据,再由已有算法鉴定类TAD域结构的新算法scHiCluster及Higashi六个软件进行综合比较,发现用deTOKI分析单细胞Hi-C数据结果优于其他六个软件。研究比较的内容主要基于两点,首先是将高分辨率水平的Hi-C数据进行下采样,比较下采样数据和原始数据中鉴定的类TAD域结构的相似度,然后对染色质结构进行三维建模,对各个模型分别生成高分辨率水平和单细胞水平的模拟Hi-C数据,比较两个数据中鉴定的类TAD域结构的相似度。该研究还在已有的单细胞Hi-C实验数据上使用模块系数和结构熵等指标来评价软件的表现,deTOKI均优于其他算法。
新算法deTOKI有助于未来的单细胞内染色质高级结构的研究,基于deTOKI算法,研究发现了单细胞内的类TAD域结构和细胞类型的关系,以及其与组蛋白修饰、DNA甲基化等多组学数据的关联。该研究丰富了关于基因组结构和功能关系的认识,为三维基因组学研究提供了新思路。
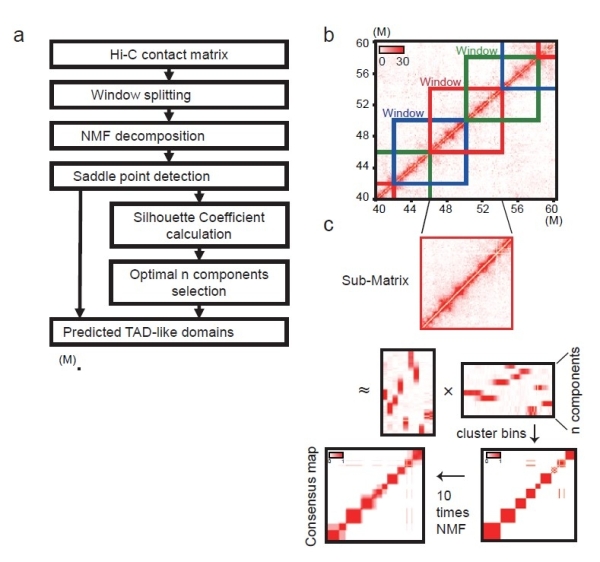
deTOKI的算法流程
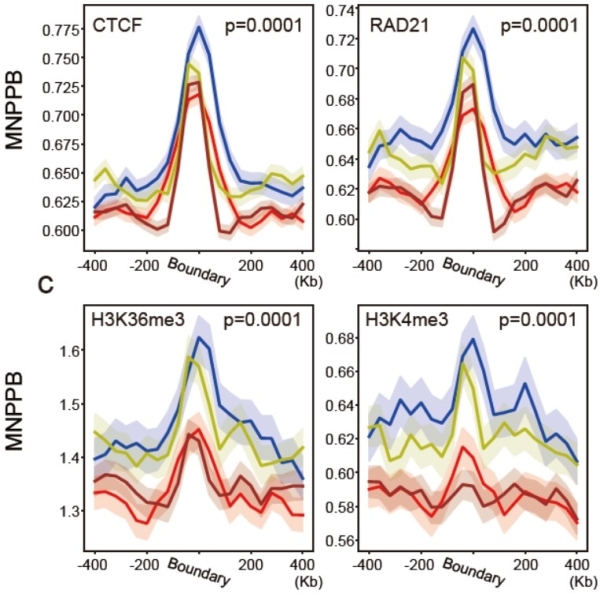
单细胞水平类TAD边界的表观修饰分布
扫一扫在手机打开当前页

© 1996 - 中国科学院 版权所有 京ICP备05002857号-1  京公网安备110402500047号 网站标识码bm48000002
京公网安备110402500047号 网站标识码bm48000002
地址:北京市西城区三里河路52号 邮编:100864
电话: 86 10 68597114(总机) 86 10 68597289(总值班室)














